CRISPR
 | |
| Math | DNA sequence |
|---|---|
| Dyddiad darganfod | 1987 |

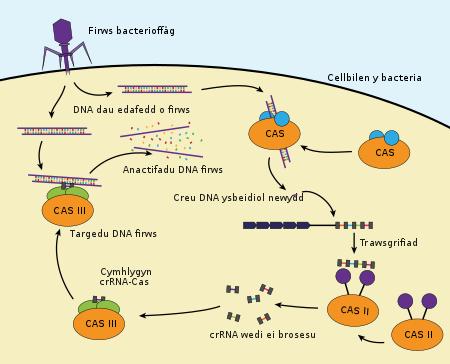
Teulu o ddilyniannau DNA mewn bacteria yw CRISPR (/ˈkrɪspr/). Mae'r dilyniannau yn cynnwys darnau DNA o firwsau sydd wedi ymosod ar y bacteria. Mae'r bacteria wedyn yn defnyddio'r darnau DNA yma i ddarganfod a dinistrio DNA mewn ymosodiadau eraill gan firwsau tebyg. Mae dilyniannau CRISPR yn rhan bwysig o system amddiffyn bacteria.[1] Maen nhw hefyd yn cael eu defnyddio fel rhan o dechnoleg o'r enw CRISPR/Cas9 sy'n gallu newid genynnau mewn organebau mewn ffordd effeithiol a manwl.[2]
System imiwnedd mewn organebau procaryotig yw CRISPR/Cas. Mae'n system sy'n rhoi ymwrthedd rhag elfennau genetig dieithr, megis y rheiny sy'n bresennol mewn plasmidau o facteria eraill ac mewn firwsau bacterioffag.[3][4][5] Maen nhw'n darparu math o imiwnedd caffaeledig i'r bacteria. Mae RNA sy'n dal y dilyniant o'r ymosodwyr blaenorol yn helpu proteinau Cas i ddarganfod a thorri DNA dieithr. Call proteinau Cas eraill, hefyd wedi eu harwain gan RNA, dorri RNA dieithr fel a geir yn lle DNA mewn rhai firwsau.[6] Fe welir dilyniannau CRISPR mewn tua 40% o'r genomau bacteriaidd sydd wedi eu dilyniannu, ac mewn 90% o archaea sydd wedi eu dilyniannu.[7]
Daw'r talfyriad CRISPR o'r enw Saesneg - Clustered Regularly Interspaced Short Palindromic Repeats.[8] Bathwyd yr enw pan nad oedd gwyddonwyr yn gwybod am darddiad a defnydd is-ddilyniannau ysbeidiol. Ar y pryd, disgrifwyd CRISPR fel darnau o DNA procaryotig yn cynnwys dilyniannau byr, ailadroddol. Mewn dilyniannau ailadroddol palindromig, mae dilyniant y niwcleotidau yr un fath yn y ddau gyfeiriad. Dilynnir pob adran ailadroddol gan ddarnau byr o ddarnau DNA ysbeidiol o ymosodiadau blaenorol i DNA dieithr (ee firws neu blasmid).[9] Ceir clystyrau bychain o enynnau cas (system yn gysylltiedig â CRISPR) o gwmpas dilyniannau CRISPR.
Mae fersiwn syml o system CRISPR/Cas, o'r enw CRISPR/Cas9, wedi ei addasu i olygu genomau. Wrth ddanfon yr ensym niwcleas Cas9 wedi ei gyfuno ag RNA arwain (gRNA) synthetig i mewn i gell, gellir torri genom y gell mewn man dewisiol, gan ganiatau dileu genynnau a/neu ychwaneug genynnau newydd.[10] Mae'r cymhlygyn Cas9-gRNA yn cyfateb â'r cymhlygyn CAS III-crRNA yn y diagram uchod mewn bacteria.
Mae gan dechnegau golygu genom CRISPR/CAS lawer o ddefnyddiau posibl, yn cynnwys mewn meddygaeth ac mewn gwella cnydau. Cyhoeddwyd yn 2015 mai system olygu genom CRISPR/Cas9-gRNA[11][12] oedd dewis cymdeithas y AAAS fel darganfyddiad gwyddonol y flwyddyn.[13] Mae rhai pryderon ethegol wedi eu crybwyll ynglŷn â defnyddio CRISPR ar gyfer golygu'r llinach genhedlu.[14]
Hanes
[golygu | golygu cod]Dechreuodd daranfyddiad darnau ailadroddol o DNA mewn tri rhan o'r byd.
Dilyniannau ailadroddol
[golygu | golygu cod]Daeth y disgrifiad cyntaf o beth sydd erbyn hyn yn cael ei alw'n CRISPR o ymchwilydd ym Mhrifysgol Osaka, Yoshizumi Ishino, yn 1987. Ar gamgymeriad, fe gloniodd ran o ddilyniant CRISPR ynghyd â genyn iap, y terged oedd Ishino â diddordeb ynddo. Roedd trefniant y dilyniannau ailadroddol yn anarferol - fel arfer, mae dilyniannau ailadroddol wedi eu trefnu yn olynol ar hyd dilyniannau DNA, heb ymyriadau rhyngddynt. Doedd gwyddonwyr ar y pryd ddim yn gwybod beth oedd swyddogaeth dilyniannau ailadroddol ysbeidiol mewn clystyrau.[15]
Yn 1993, cyhoeddodd ymchwilwyr yn yr Iseldiroedd oedd yn gweithio ar Mycobacterium tuberculosis (y bacteria sy'n achosi twbercwlosis neu'r diciâu) ddwy erthygl am glwstwr o ddilyniannau ailadroddol uniongyrchol â darnau eraill o DNA rhyngddynt yn y bacteriwm. Fe welodd yr ymchwilwyr fod y darnau DNA ysbeidiol yma yn amrywio yn arw rhwng straenau gwahanol o M. tuberculosis.[16] Fe ddefnyddion nhw'r nodwedd yma i ddatblygu dull o ddosbarthu'r straenau, ac mae'r dull yma - spoligotyping - yn cael ei ddefnyddio hyd heddiw.[17][18]
Ar yr un pryd, gwelwyd dilyniannau ailadroddol yn y rhywogaethau archaea Haloferax a Haloarcula. Dechreuodd Francisco Mojica astudio swyddogaeth y dilyniannau ailadroddol yma ym Mhrifysgol Alicante yn Sbaen. Er fod ei ragdybiaeth wreiddiol yn anghywir, dyfalodd Mojica ar y pryd fod y clystyrau yma o ddilyniannau ailadroddol yn bwysig ar gyfer didoli DNA datblygedig i mewn i epigelloedd yn ystod cellraniad oherwydd nad all blasmidau a chromosomau â dilyniannau o'r un fath gydfodoli yn Haloferax volcanii. Gwelodd Mojica hefyd drawsgrifiad y dilyniannau ailadroddol bylchog am y tro cyntaf.[19] Erbyn 2000, roedd grŵp ymchwil Mojica wedi dynodi dilyniannau ailadroddom bylchog mewn 20 rhywogaeth o ficrobau.[20] Yn 2001, cynnigwyd y term CRISPR am y tro cyntaf gan Mojica a Ruud Jansen (roedd Jansen hefyd yn chwilio am ddilyniannau tebyg) er mwyn lleihau'r dryswch ynglŷn â'r talfyriadau gwahanol oedd yn cael eu defnyddio mewn erthyglau gwyddonol.[21]
Systemau Cas (CRISPR-associated systems)
[golygu | golygu cod]Daeth gwelliant mawr yn nealltwriaeth gwyddonwyr o CRISPR pan sylweddolodd Jansen fod genynnau arbenning bob amser i'w gweld ynghyd â'r clystyrau a welodd o ddilyniannau ailadroddol. Rhoddwyd yr enw CRISPR-associated systems, neu cas, ar y genynnau yma. Gwelodd Jansen bedwar genyn cas yn gyntaf (cas 1 i 4. Roedd gan y proteinau Cas fotiffau helicas a niwcleas, gan awgrymu eu bod yn bwysig ar gyfer strwythur dynamig y locws CRISPR.[22] Hwn oedd y cyhoeddiad lle bathwyd yr enw CRISPR fel enw cyffredinol y patrwm. Ond parhaodd swyddogaeth CRISPR i fod yn ddirgelwch.

Yn 2005, dangosodd tri grwp ymchwil annibynnol fod rhai dilyniannau ysbeidiol CRISPR wedi dod o DNA bacterioffag a DNA o du allan i'r cromosom, megis plasmidau.[24][25][26] I bob pwrpas, tameidiau o DNA sydd wedi ceisio ymosod ar y gell yn flaenorol yw'r dilyniannau ysbeidiol yma. Roedd y darganfyddiad hwn yn arwydd y gallai system CRISPR/cas chwarae rhan yn imiwnedd ymaddasol bacteria.[27] Yn gyntaf, fe wrthododd y cylchgronau gwyddonol mwyaf enwog bob un o'r tri gwaith ymchwil, ond fe'u cyhoeddwyd yn ddiweddarach mewn cylchgronau eraill.[28]
Cyhoeddwyd yr erthygl gyntaf i gynnig y gall CRISPR-Cas chwarae rhan mewn imiwnedd mewn microbau gan grŵp Mojica yn 2005. Rhagdybiodd Mojica y gallai trawsgrifiad RNA y dilyniannau ysbeidiol chwarae rhan gan alluogi'r system i adnabod targed y protein Cas. Byddai mecanwaith o'r fath yn cyfateb i system ymyriant RNA mewn celloedd ewcaryotig. Felly, yr un pryd ag y daeth Ian Wilmut yn enwog am glônio Dolly'r ddafad,[29][30] estynodd Koonin a'i gydweithwyr (2005) y rhagdybiaeth ymyriad RNA gan gynnig dulliau gweithio ar gyfer yr is-fathau gwahanol o CRISPR-Cas yn ôl swyddogaeth rhagweliedig eu proteinau.[31] Cynnigiodd eraill fod y dilyniannau CRISPR yn arwain ensymau Cas i ddiraddio DNA firysau.
Dangosodd gwaith ymchwil o lawer o grwpiau gwahanol y mecanweithiau sylfaenol wrth wraidd imiwnedd CRISPR-Cas. Yn 2007, cyhoeddwyd y dystiolaeth arbrofol gyntaf mai system imiwnedd ymaddasol oedd CRISPR. Caffaelodd locws CRISPR yn Streptococcus thermophilus ddilyniannau ysbeidiol o DNA firws oedd yn ymosod arno. Llwyddodd yr ymchwilwyr i newid ymwrthedd S. thermophilus i firws bacterioffag gan ychwanegu a dileu dilyniannau ysbeidiol wedi eu canfod mewn firysau gwahanol.[32] Yn 2008, dynododd Brouns a chydweithwyr gymhlygyn protein Cas mewn E. coli oedd yn gallu torri'r RNA CRISPR o fewn i'r dilyniannau ailadroddol i mewn i foleciwlau RNA yn cynnwys dilyniannau ysbeidiol; fe welodd yr ymchwilwyr fod o moleciwlau yma yn aros ynghlwm i'r cymhlygyn protein. Yr un flwyddyn, dangosodd Marraffini a Sontheimer ddilyniant CRISPR yn S. epidermidis oedd yn targedu DNA yn hytrach nag RNA er mwyn atal cyfunedd. Doedd y darganfyddiad hwn ddim yn cydfynd â'r syniad fod mecanwaith imiwnedd CRISPR-Cas yn debyg i system ymyriad RNA, er y darganfyddwyd system CRISPR-Cas oedd yn targedu RNA dieithr yn ddiweddarach mewn Pyrococcus furiosus. Dangosodd gwaith yn 2010 fod CRISPR-Cas yn torri'r ddau edafedd o DNA firysau bacterioffag a phlasmidau yn S. thermophilus.[33]
Cas9
[golygu | golygu cod]Dechreuodd ymchwilwyr astudio system CRISPR mwy syml o Streptococcus pyogenes sy'n defnyddio'r protein Cas9. Mae pedwar rhan i system endoniwcleas Cas9, sy'n cynnwys dau foleciwl RNA bychan o'r enw RNA CRISPR (crRNA) ac RNA CRISPR traws-ysgogi (tracrRNA).[34] Llwyddodd Jennifer Doudna ac Emmanuelle Charpentier i ailadeiladu a symleiddio'r endoniwcleas Cas9 gan gyduno'r ddau foleciwl RNA i ffurfio un RNA arwain. Gall Cas9 wedyn, pan wedi ei gyfuno â'r RNA arwain, ddarganfod a thorri targed penodol mewn DNA wedi ei ddynodi gan yr RNA arwain. Gan newid dilyniant niwcleotid yr RNA arwain, gellid rhaglennu'r system Cas9 i dargedu unrhyw ddilyniant DNA er mwyn ei dorri. Dangosodd grŵp arall o gydweithwyr, yn cynnwys Šikšnys, Gasiūnas, Barrangou a Horvath y gallant hefyd ail-ragnlennu'r Cas9 o system CRISPR S. thermophilus er mwyn targedu man o'u dewis gan newid ei ddilyniant crRNA. Rhoddodd y datblygiadau hyn hwb i ymdrechion gwyddonwyr i olygu genomau gen ddefnyddio'r system CRISPR-Cas9.
Dangosodd dau grŵp ymchwil ar yr un pryd a'i gilydd y gellid defnyddio CRISPR/Cas9 er mwyn golygu'r genom dynol mewn celloedd meithrin.[35][36][37] Ers hynny, mae'r system wedi ei defnyddio mewn ystod eang o organebau, gan gynnwys burum pobi (Saccharomyces cerevisiae),[38][39][40] pysgod rhesog (D. rerio),[41] pryfed ffrwythau (Drosophila melanogaster),[42] nematodau (C. elegans),[43] planhigion,[44] llygod,[45] mwncïod[46] ac ebryonau dynol.
Mae CRISPR hefyd wedi ei addasu ar gyfer creu ffactorau trawsgrifiad y gellir eu rhaglennu. Gan ddefnyddio'r rhain, gall wyddonwyr dargedu a throi genynnau penodol ymlaen neu i ffwrdd.[47]
Defnyddiau
[golygu | golygu cod]Erbyn diwedd 2014, roedd oddeutu 1000 o erthyglau ymchwil yn crybwyll CRISPR wedi eu cyhoeddi.[48][49] Mae'r dechnoleg wedi ei defnyddio er mwyn diffodd genynnnau mewn celloedd a llinachau o gelloedd dynol, i astudio Candida albicans, i addasu'r burum sy'n cael ei ddefnyddio i greu biodanwydd, ac ar gyfer addasu genetig mewn cnydau. Gellir defnyddio CRISPR hefyd i newid mosgitos fel nad allant drosglwyddo afiechydon megis malaria.[50]
Peiriannu'r genom
[golygu | golygu cod]Mae systemau golygu genom CRISPR/Cas9 yn defnyddio system CRISPR Math II. Pan gaiff ei defnyddio ar gyfer golygu genom, mae'r system yn cynnwys Cas9, crRNA, tracrRNA ac adran opsiynol o dempled atgyweirio DNA.

Prif gydrannau
[golygu | golygu cod]| Cydran | Swyddogaeth |
|---|---|
| crRNA | Yn cynnwys yr RNA arwain sy'n lleoli'r adran gywir o DNA y targed, ynghyd â safle sy'n clymu'r moleciwl i'r tracrRNA i ffurfio cymhlygyn gweithredol. |
| tracrRNA | Yn clymu i'r crRNA i ffurfio cymhlygyn gweithredol. |
| sgRNA | RNA arwain unigol. RNA cyfunedig sy'n cynnwys tracrRNA ac oleiaf un crRNA. |
| Cas9 | Yn ei ffurf weithredol, gall y protein hwn addasu DNA. Gall mathau gwahanol o Cas9 weithredu mewn ffyrdd gwahanol (hy rhicio un edafedd, torri'r ddau edafedd neu glymu at DNA). |
| Templed atgyweirio |
DNA i arwain y broses atgyweirio DNA, gan alluogi ychwanegu dilyniant newydd i'r bwlch ar ôl i Cas9 dorri DNA y targed. |
Cyfeiriadau
[golygu | golygu cod]- ↑ "The roles of CRISPR-Cas systems in adaptive immunity and beyond". Current Opinion in Immunology 32: 36–41. 2015. doi:10.1016/j.coi.2014.12.008. PMID 25574773.
- ↑ "CRISPR/Cas9 for genome editing: progress, implications and challenges". Human Molecular Genetics 23 (R1): R40–6. 2014. doi:10.1093/hmg/ddu125. PMID 24651067.
- ↑ "What is CRISPR/Cas9?". Archives of Disease in Childhood. Education and Practice Edition 101 (4): 213–5. Awst 2016. doi:10.1136/archdischild-2016-310459. PMC 4975809. PMID 27059283. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4975809.
- ↑ "CRISPR provides acquired resistance against viruses in prokaryotes". Science 315 (5819): 1709–12. Mawrth 2007. Bibcode 2007Sci...315.1709B. doi:10.1126/science.1138140. PMID 17379808. (registration required)
- ↑ "CRISPR interference limits horizontal gene transfer in staphylococci by targeting DNA". Science 322 (5909): 1843–5. Rhagfyr 2008. Bibcode 2008Sci...322.1843M. doi:10.1126/science.1165771. PMC 2695655. PMID 19095942. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=2695655.
- ↑ "Diverse evolutionary roots and mechanistic variations of the CRISPR-Cas systems". Science 353 (6299): aad5147. 2016. doi:10.1126/science.aad5147. PMID 27493190.
- ↑ "The CRISPRdb database and tools to display CRISPRs and to generate dictionaries of spacers and repeats". BMC Bioinformatics 8: 172. Mai 2007. doi:10.1186/1471-2105-8-172. PMC 1892036. PMID 17521438. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=1892036.
- ↑ Sawyer, Eric (9 Chwefror 2013). "Editing Genomes with the Bacterial Immune System". Scitable. Nature Publishing Group. Cyrchwyd 6 Ebrill 2015.
- ↑ "CRISPR interference: RNA-directed adaptive immunity in bacteria and archaea". Nature Reviews Genetics 11 (3): 181–90. Mawrth 2010. doi:10.1038/nrg2749. PMC 2928866. PMID 20125085. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=2928866.
- ↑ "Chemically modified guide RNAs enhance CRISPR-Cas genome editing in human primary cells". Nature Biotechnology 33 (9): 985–9. Medi 2015. doi:10.1038/nbt.3290. PMC 4729442. PMID 26121415. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4729442.
- ↑ "CRISPR: gene editing is just the beginning". Nature 531 (7593): 156–9. Mawrth 2016. doi:10.1038/531156a. PMID 26961639.
- ↑ Maxmen, Amy (Awst 2015). "The Genesis Engine". WIRED. Cyrchwyd 2016-06-05.
- ↑ "Breakthrough of the Year: CRISPR makes the cut". Science Magazine. American Association for the Advancement of Science. 17 Rhagfyr 2015.
- ↑ "CRISPR, the disruptor". Nature 522 (7554): 20–4. Mehefin 2015. doi:10.1038/522020a. PMID 26040877.
- ↑ "Nucleotide sequence of the iap gene, responsible for alkaline phosphatase isozyme conversion in Escherichia coli, and identification of the gene product". Journal of Bacteriology 169 (12): 5429–33. Rhagfyr 1987. PMC 213968. PMID 3316184. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=213968.
- ↑ "Comparison of various repetitive DNA elements as genetic markers for strain differentiation and epidemiology of Mycobacterium tuberculosis". Journal of Clinical Microbiology 31 (8): 1987–95. Awst 1993. PMC 265684. PMID 7690367. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=265684.
- ↑ "Nature of DNA polymorphism in the direct repeat cluster of Mycobacterium tuberculosis; application for strain differentiation by a novel typing method". Molecular Microbiology 10 (5): 1057–65. Rhagfyr 1993. doi:10.1111/j.1365-2958.1993.tb00976.x. PMID 7934856. https://archive.org/details/sim_molecular-microbiology_1993-12_10_5/page/1057.
- ↑ "On the Origin of CRISPR-Cas Technology: From Prokaryotes to Mammals". Trends in Microbiology 24 (10): 811–20. 2016. doi:10.1016/j.tim.2016.06.005. PMID 27401123.
- ↑ "The discovery of CRISPR in archaea and bacteria". The FEBS Journal 283 (17): 3162–9. 2016. doi:10.1111/febs.13766. PMID 27234458.
- ↑ "Biological significance of a family of regularly spaced repeats in the genomes of Archaea, Bacteria and mitochondria". Molecular Microbiology 36 (1): 244–6. Ebrill 2000. doi:10.1046/j.1365-2958.2000.01838.x. PMID 10760181.
- ↑ Barrangou, Rodolphe; van der Oost, John (2013). CRISPR-Cas Systems : RNA-mediated Adaptive Immunity in Bacteria and Archaea. Heidelberg: Springer. t. 6. ISBN 978-3-642-34656-9.
- ↑ "Identification of genes that are associated with DNA repeats in prokaryotes". Molecular Microbiology 43 (6): 1565–75. Mawrth 2002. doi:10.1046/j.1365-2958.2002.02839.x. PMID 11952905.
- ↑ "CRISPR/Cas, the immune system of bacteria and archaea". Science 327 (5962): 167–70. Ionawr 2010. Bibcode 2010Sci...327..167H. doi:10.1126/Science.1179555. PMID 20056882.
- ↑ "CRISPR elements in Yersinia pestis acquire new repeats by preferential uptake of bacteriophage DNA, and provide additional tools for evolutionary studies". Microbiology 151 (Pt 3): 653–63. Mawrth 2005. doi:10.1099/mic.0.27437-0. PMID 15758212.
- ↑ "Intervening sequences of regularly spaced prokaryotic repeats derive from foreign genetic elements". Journal of Molecular Evolution 60 (2): 174–82. Chwefror 2005. doi:10.1007/s00239-004-0046-3. PMID 15791728. https://archive.org/details/sim_journal-of-molecular-evolution_2005-02_60_2/page/174.
- ↑ "Clustered regularly interspaced short palindrome repeats (CRISPRs) have spacers of extrachromosomal origin". Microbiology 151 (Pt 8): 2551–61. Awst 2005. doi:10.1099/mic.0.28048-0. PMID 16079334.
- ↑ "What history tells us XXXVII. CRISPR-Cas: The discovery of an immune system in prokaryotes". Journal of Biosciences 40 (2): 221–3. Mehefin 2015. doi:10.1007/s12038-015-9532-6. PMID 25963251.
- ↑ "The Heroes of CRISPR". Cell 164 (1–2): 18–28. Ionawr 2016. doi:10.1016/j.cell.2015.12.041. PMID 26771483.
- ↑ Ledford, Heidi (2017). "Five big mysteries about CRISPR's origins". Nature 541 (7637): 280–282. Bibcode 2017Natur.541..280L. doi:10.1038/541280a. PMID 28102279.
- ↑ "for the prediction of CRISPR function". Archifwyd o'r gwreiddiol ar 2017-11-22. Cyrchwyd 2017-11-17.
- ↑ "A putative RNA-interference-based immune system in prokaryotes: computational analysis of the predicted enzymatic machinery, functional analogies with eukaryotic RNAi, and hypothetical mechanisms of action". Biology Direct 1: 7. Mawrth 2006. doi:10.1186/1745-6150-1-7. PMC 1462988. PMID 16545108. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=1462988.
- ↑ "The CRISPR craze". Science 341 (6148): 833–6. Awst 2013. doi:10.1126/science.341.6148.833. PMID 23970676.
- ↑ "The CRISPR/Cas bacterial immune system cleaves bacteriophage and plasmid DNA". Nature 468 (7320): 67–71. Tachwedd 2010. doi:10.1038/nature09523. PMID 21048762.
- ↑ "Diversity of CRISPR-Cas immune systems and molecular machines". Genome Biology 16: 247. Tachwedd 2015. doi:10.1186/s13059-015-0816-9. PMC 4638107. PMID 26549499. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4638107.
- ↑ "Development and applications of CRISPR-Cas9 for genome engineering". Cell 157 (6): 1262–78. Mehefin 2014. doi:10.1016/j.cell.2014.05.010. PMC 4343198. PMID 24906146. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4343198.
- ↑ "Multiplex genome engineering using CRISPR/Cas systems". Science 339 (6121): 819–23. Chwefror 2013. doi:10.1126/science.1231143. PMC 3795411. PMID 23287718. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3795411.
- ↑ "RNA-guided human genome engineering via Cas9". Science 339 (6121): 823–6. Chwefror 2013. doi:10.1126/science.1232033. PMC 3712628. PMID 23287722. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3712628.
- ↑ "Genome engineering in Saccharomyces cerevisiae using CRISPR-Cas systems". Nucleic Acids Research 41 (7): 4336–43. Ebrill 2013. doi:10.1093/nar/gkt135. PMC 3627607. PMID 23460208. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3627607.
- ↑ "Construction of a quadruple auxotrophic mutant of an industrial polyploid saccharomyces cerevisiae strain by using RNA-guided Cas9 nuclease". Applied and Environmental Microbiology 80 (24): 7694–701. Rhagfyr 2014. doi:10.1128/AEM.02310-14. PMC 4249234. PMID 25281382. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4249234.
- ↑ "Metabolic Engineering of Probiotic Saccharomyces boulardii". Applied and Environmental Microbiology 82 (8): 2280–7. Ebrill 2016. doi:10.1128/AEM.00057-16. PMC 4959471. PMID 26850302. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4959471.
- ↑ "Efficient genome editing in zebrafish using a CRISPR-Cas system". Nature Biotechnology 31 (3): 227–9. Mawrth 2013. doi:10.1038/nbt.2501. PMC 3686313. PMID 23360964. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3686313.
- ↑ "Genome engineering of Drosophila with the CRISPR RNA-guided Cas9 nuclease". Genetics 194 (4): 1029–35. Awst 2013. doi:10.1534/genetics.113.152710. PMC 3730909. PMID 23709638. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3730909.
- ↑ "Heritable genome editing in C. elegans via a CRISPR-Cas9 system". Nature Methods 10 (8): 741–3. Awst 2013. doi:10.1038/nmeth.2532. PMC 3822328. PMID 23817069. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3822328.
- ↑ "Demonstration of CRISPR/Cas9/sgRNA-mediated targeted gene modification in Arabidopsis, tobacco, sorghum and rice". Nucleic Acids Research 41 (20): e188. Tachwedd 2013. doi:10.1093/nar/gkt780. PMC 3814374. PMID 23999092. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3814374.
- ↑ "One-step generation of mice carrying mutations in multiple genes by CRISPR/Cas-mediated genome engineering". Cell 153 (4): 910–8. Mai 2013. doi:10.1016/j.cell.2013.04.025. PMC 3969854. PMID 23643243. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3969854.
- ↑ "Targeted genome editing in primate embryos". Cell Research 25 (7): 767–8. Gorffennaf 2015. doi:10.1038/cr.2015.64. PMC 4493275. PMID 26032266. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=4493275.
- ↑ "CRISPR interference (CRISPRi) for sequence-specific control of gene expression". Nature Protocols 8 (11): 2180–96. Tachwedd 2013. doi:10.1038/nprot.2013.132. PMC 3922765. PMID 24136345. http://www.pubmedcentral.nih.gov/articlerender.fcgi?tool=pmcentrez&artid=3922765.
- ↑ Doudna, J. A; Charpentier, E (2014). "The new frontier of genome engineering with CRISPR-Cas9". Science 346 (6213): 1258096. doi:10.1126/science.1258096. PMID 25430774.
- ↑ "CRISPR, the disruptor". Nature 522 (7554): 20–4. Mehefin 2015. Bibcode 2015Natur.522...20L. doi:10.1038/522020a. PMID 26040877.
- ↑ "Can CRISPR-Cas9 gene drives curb malaria?". Nature Biotechnology 34 (2): 149–50. 2016. doi:10.1038/nbt.3473. PMID 26849518.
- ↑ "CRISPR/Cas9 Plasmids". www.systembio.com. Archifwyd o'r gwreiddiol ar 2015-12-22. Cyrchwyd 2015-12-17.
- ↑ "CRISPR Cas9 Genome Editing". www.origene.com. OriGene. Cyrchwyd 2015-12-17.
